终于可以引用SeekSoulOnline啦!
基于选定的参数模板和配色方案,平台支持从数据过滤、批量效应去除、降维聚类到细胞注释、差异基因表达和富集分析(Fig.1).此外,该平台还提供详细的用户指南、参数描述、视频、常见问题(FAQ)和在线客户服务支持,帮助用户在分析过程中获得必要的帮助和支持。该平台支持完整的分析管道,从细胞过滤、批量效应去除、聚类、细胞注释、差异基因表达 (DEG) 和富集分析,到特征分析、空间转录组数据的交互式可视化,
一、写在前面
SeekSoul Online单细胞云平台已经上线很久啦,就在近日,SeekSoulOnline以article的形式发表在期刊《The Innovation Life》上,题为"SeekSoul Online: A user-friendly bioinformatics platform focused on single-cell multi-omics analysis"。也就是说,大家用SeekSoul Online分析数据后终于可以在发文时引用啦(当然,再acknowledgement一下也不是不行)。
DOI: 10.59717/j.xinn-life.2025.10015
链接:https://www.the-innovation.org/article/doi/10.59717/j.xinn-life.2025.100156
引用: Liu X., Wu C., Pan L., et al. (2025). SeekSoul Online: A user-friendly bioinformatics platform focused on single-cell multi-omics analysis. The Innovation Life 3:100156.

完整教程可见合集:
准备好零代码发单细胞文章吧!
云平台访问链接:https://seeksoul.online/t_static/Biomamba/Biomamba.html
二、文章内容
1、简介:
单细胞数据分析面临着诸多困境,如数据量大、分析过程复杂、难以整合不同组织类型的数据以及对专业知识和计算资源高要求,这些为缺乏编程技能的研究人员带来了重大挑战。为了解决这个问题,作者开发了 SeekSoul Online (https://seeksoul.online/t_static/Biomamba/Biomamba.html),这一单细胞多组学数据分析和交互式可视化平台,无需编程基础。该平台不仅拥有用户友好的界面,更是利用模块化架构提供强大计算能力,支持单细胞转录组、单细胞免疫库数据和 SeekSpace单细胞空间转录组数据的完整分析过程。该平台通过自建的高质量参考集和人工智能技术,实现了准确的细胞类型识别。此外,SeekSoul Online还提供交互式数据分析和报告生成,允许用户实时调整分析参数并生成分析报告进行交流(开组会岂不是连PPT都省了)。该平台还提供全面的项目管理和共享功能,以促进研究团队之间的协作和知识共享。凭借自动化的数据处理工作流程和直观的用户界面,SeekSoul Online显著提高了数据分析的便利性和效率,使研究人员能够更加专注于科学发现并加速研究进展。
2、系统架构
SeekSoul Online采用现代化的三层架构设计,包括前端、后端和生物信息学,确保高性能、可扩展性和可靠性。它采用用户界面构建Vue.js框架,提供响应式和交互式客户端体验。用户可以上传数据、管理分析项目和任务,并通过用户友好的Web界面可视化结果。平台后端采用分布式文件系统(如HDFS)和MySQL数据库,确保数据稳定性和快速访问。对于数据分析,它基于Docker 实现,分析过程封装在R和Python 脚本中。计算服务利用稳定、可靠、弹性扩展的云服务器,可以根据分析任务的计算需求动态调整计算资源,确保分析过程高效、流畅。该平台根据正在处理的蜂窝数据的规模动态分配云服务器资源。
3、不要编程、不要编程、不要编程
SeekSoul Online大大简化了单细胞多组学数据分析的整个过程,从数据上传、可视化、高级分析。没有编程技能的用户也可以通过直观的界面轻松完成复杂的数据分析任务。为了保证数据分析的准确性,我们还提供了基于已发表文章和数千个项目的参数模板,以及可发布的配色方案,以确保即使是初学者也能快速准确地实现数据分析和挖掘。该平台还允许用户根据个人需求或期刊要求定制分析参数或配色方案。基于选定的参数模板和配色方案,平台支持从数据过滤、批量效应去除、降维聚类到细胞注释、差异基因表达和富集分析(Fig.1).此外,该平台还提供详细的用户指南、参数描述、视频、常见问题(FAQ)和在线客户服务支持,帮助用户在分析过程中获得必要的帮助和支持。
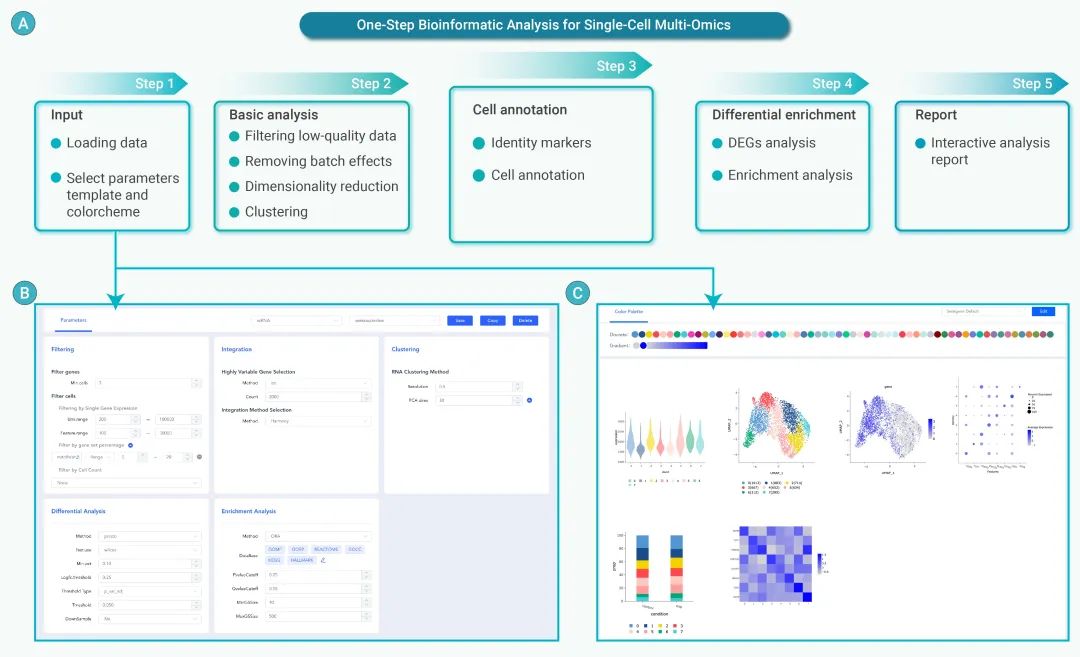
Fig.1
4、单细胞/空转分析一网打尽
SeekSoul Online为单细胞转录组数据、单细胞免疫库数据和SeekSpace单细胞空间转录组数据提供了全面的工作流程,涵盖了从数据上传到最终报告生成的所有步骤,确保用户可以在统一的平台上完成所有分析。该过程包括细胞过滤、归一化、批量效应去除、聚类、细胞注释、特征评分、空间位置信息分析和差异基因表达和富集分析,以及细胞间相互作用、伪时间、TCR、BCR和报告生成等高级分析。
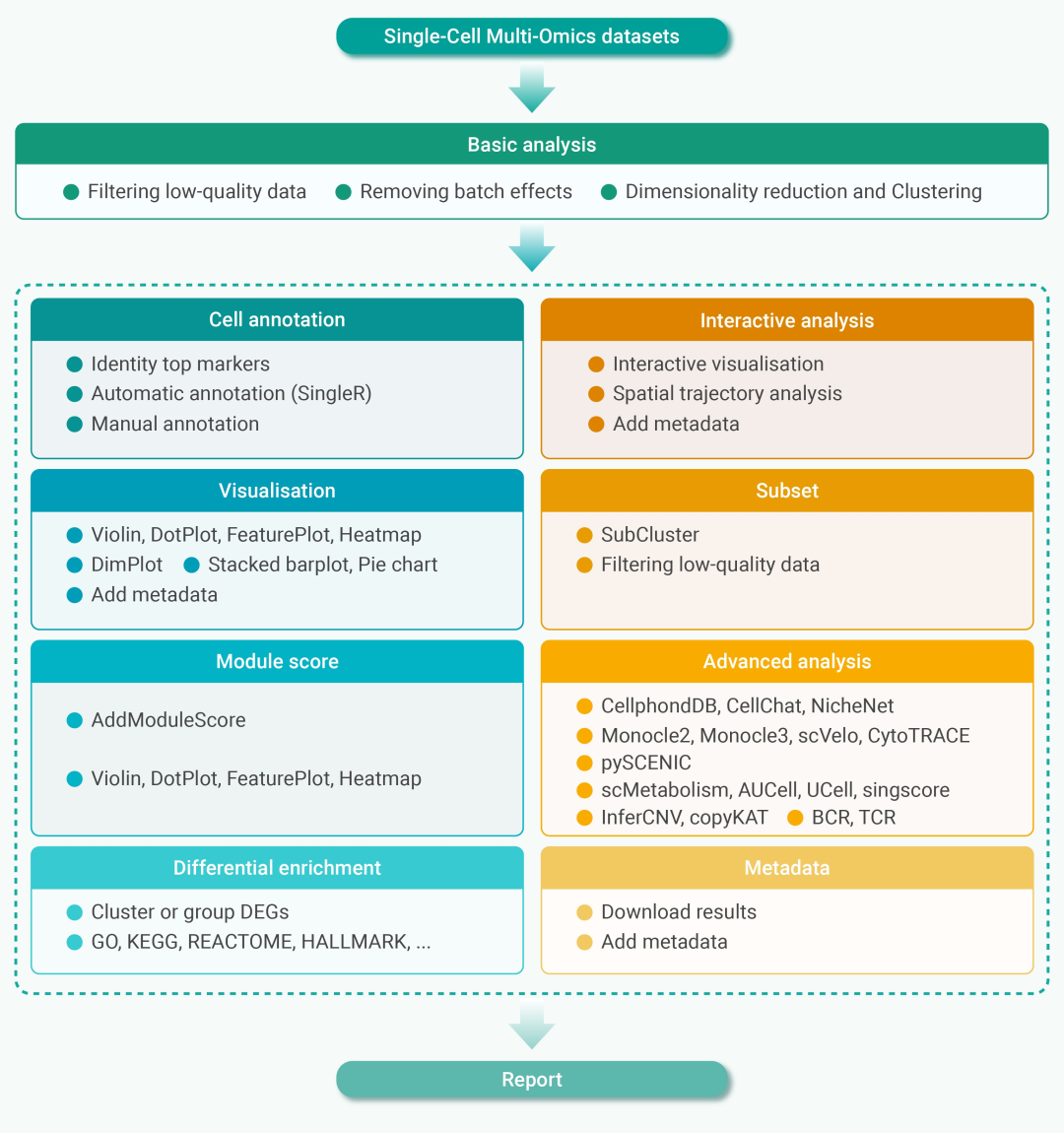
Fig.2
SeekSoul Online采用模块化设计架构,将单细胞多组学数据分析过程划分为多个独立但相互关联的功能模块。这十个模块包括基本分析、细胞注释、可视化、模块评分、差异富集、交互式分析、子集、高级分析、元数据和报告。每个模块都有独立的功能、输入和输出。用户可以根据自己的具体研究需求构建个性化的数据分析流程。当然,模块之间的无缝连接和统一的接口设计保证了不同模块之间的高效数据传输和协同工作,避免了数据丢失和不一致的问题。例如,用户可以在模块评分模块中对基因集进行评分,然后在可视化模块中可视化评分结果,依此类推。这种模块化设计不仅简化了用户的作过程,还大大增强了平台的可扩展性,允许快速集成新兴的分析工具和算法,从而成为研究人员在单细胞多组学数据分析方面的得力助手(Fig.3)
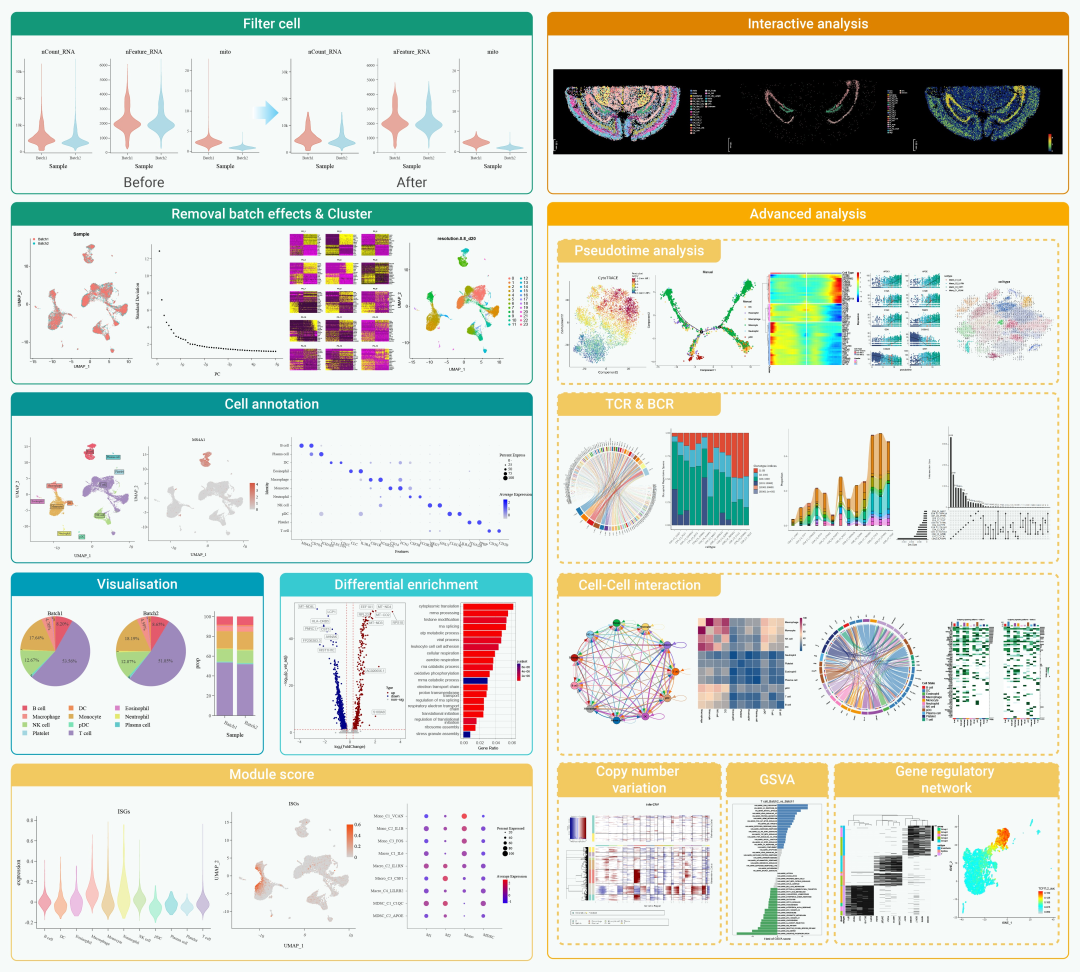
Fig.3
5.高置信度细胞注释
为了提高单细胞数据分析的准确性和可靠性,SeekSoul Online采用基于已发表文章和先进的人工智能技术构建的高质量参考集进行细胞注释。这些参考集经过严格的质量控制和人工审查,涵盖57种人体组织和46种小鼠组织。然后使用SingleR基于这些参考集执行注释,确保自动注释的准确性。此外,该平台将经典的细胞标记数据库与人工智能技术相结合,通过分析每个簇中特异性表达的基因,自动识别不同的细胞类型及其亚型。这种综合方法不仅提高了标注的自动化水平,还有效提高了结果的精度和准确度。同时,该平台允许用户在自动标注后根据标记表达式进行手动标注(Fig.4).
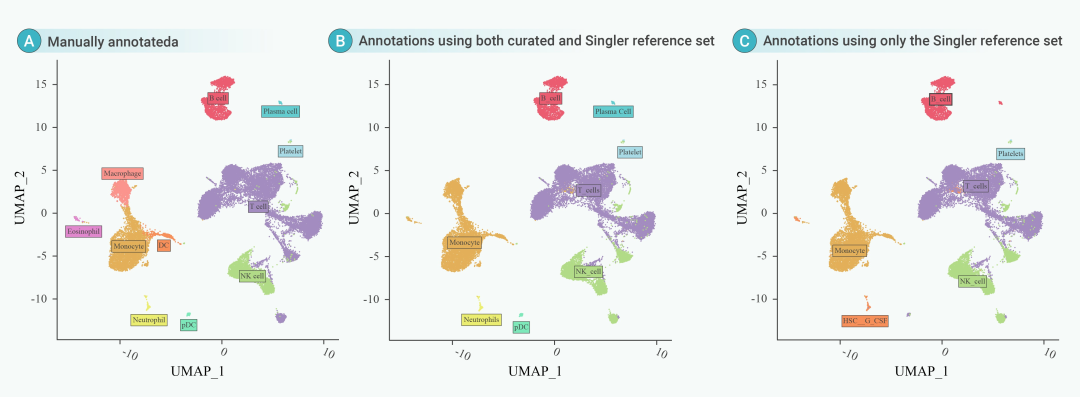
Fig.4
6.灵活的数据管理和标签定制
SeekSoul Online在单细胞多组学分析中展示了出色的元数据管理(metadata)能力。该平台支持用户根据个人需求定制细胞标签。此外,它还有效地管理单细胞数据的元数据,允许用户根据自己的研究目标或实验设计上传、编辑、过滤、合并和定制细胞标签。例如,在SeekSpace中进行肿瘤微环境分析时,用户可以将疾病组中的特定细胞类型或定位于特定空间区域的细胞定义为新的细胞亚型,实现对疾病特征和细胞功能的更精确分析。此外,我们还可以合并主组和子组的注释结果,以确保数据的完整性,这使得下游分析(例如细胞间通讯)能够在完整的细胞图谱上进行。这种灵活高效的元数据管理能力不仅提高了数据分析的深度和准确性,还显著增强了平台对多样化研究需求的适应性和实用性。
Fig.5
7.交互式分析和可共享报告
SeekSoul Online的交互式分析和报告生成功能显著增强了分析过程中实时参数调整、结果汇总和沟通的便利性。在数据分析阶段,用户可以将多个分析结果进行组合和比较,以可视化不同的分析方法和参数设置对结果的影响。可视化模块集成了多种动态图表和可视化图,包括散点图、点图、小提琴图、热图、饼图和堆积条形图。用户可以实时调整绘图参数,例如颜色和比例,以生成发表级的高质量图像。此外,SeekSoul Online的交互式报告生成功能允许用户对分析结果进行总结和组织,以创建个性化的报告,这极大地方便了结果的共享和沟通。这些特征的整合不仅提高了数据分析的透明度和可解释性,还促进了研究团队之间的协作和知识共享。
8.项目管理和多用户协作分析
SeekSoul Online在项目管理和协作分析方面也表现出显著优势。它支持研究团队之间的高效协作和数据共享,有效提高研究工作的效率和质量。该平台为每个项目提供了独立且结构化的管理空间,允许用户创建和管理多个分析项目。用户可以创建、编辑和存储与项目相关的各种信息,例如样本详细信息和数据源,确保项目信息的完整性和可追溯性。此外,它还支持项目负责人为每个项目分配不同的用户权限,确保数据和分析过程的安全性和隐私性。通过项目管理功能,团队成员可以实时跟踪项目进度,及时沟通和解决分析挑战,分享成果和研究思路。这种高效的协作机制打破了传统科研中的信息孤岛,促进了团队成员之间的紧密合作,提高了研究成果。
四、案例研究:在人类食管鳞状细胞癌微环境中再现关键发现、
SeekSoul Online平台为研究人员提供了各种应用场景的全面支持。用户只需点击一下即可完成细胞类型注释、免疫细胞功能评估、交互式可视化等。为了展示SeekSoul Online平台在真实世界研究中的价值,作者以已发表的食管鳞状细胞癌 (ESCC) 微环境研究数据集为例。这证明了SeekSoul Online平台无需编写代码即可获得与顶级期刊上发表的分析结果相当的分析结果的能力:
1、数据下载和处理。
用户可以从示例文章中提供的登录号下载矩阵数据:GSE160269。在SeekSoul Online中,下载的矩阵文件(包括 barcodes.tsv.gz、features.tsv.gz 和 matrix.mtx.gz)通过数据上传功能作为 zip 文件上传。平台自动执行数据格式验证。为了适应多样化的用户需求,该平台还支持 HDF5 (.h5)、SeuratObject (.rds)、AnnData (.h5ad) 等数据格式。
2、分析工作流程。
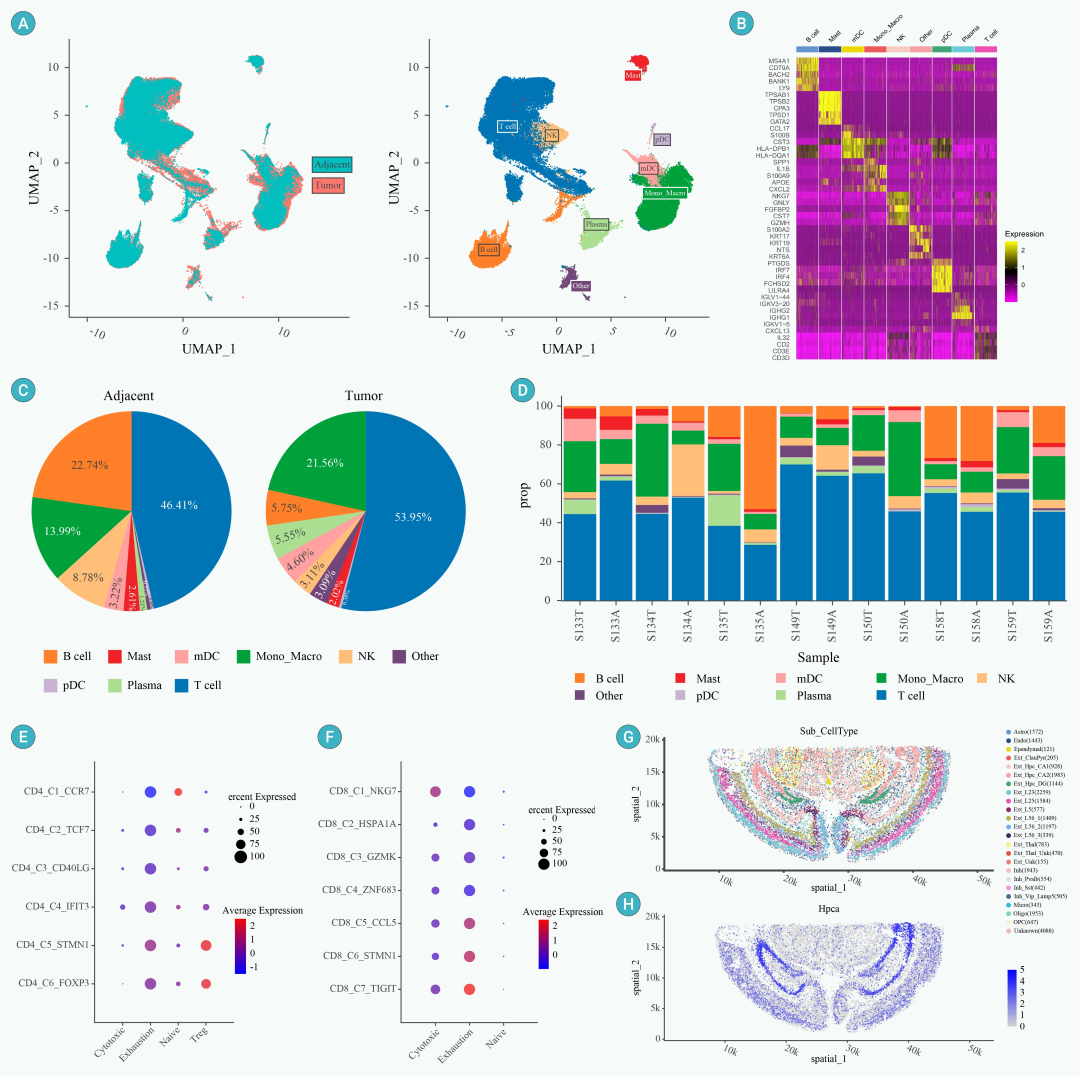
(1)质量控制和预处理:在基础分析模块中,设置过滤参数(nFeature:400-6000,线粒体基因比率阈值:10%)去除低质量细胞。在整合部分,选择前 2000 个高度可变的基因,并使用 Harmony 方法去除批量效应 (Fig.6)。
(2)细胞类型注释:基于文章中提到的经典标记基因(如CD3D、CD19、IGHG1等),通过细胞注释模块鉴定出T细胞、B细胞、浆细胞等8种主要细胞类型
(3)可视化:使用可视化模块,用户可以生成经典图形,如降维图、点图、热图等。还可以绘制饼图和堆叠条形图来比较肿瘤和邻近组织中细胞类型的比例(Fig.6C-D)。
(4)亚型分析:使用“子集”模块,可以选择T细胞和NK细胞进行额外的降维、聚类和注释。然后可以使用文章中的基因集进行特征分析,以探索细胞亚型的功能和特征(Fig.6E-F)。结果表明,该平台成功再现了原文的主要发现,包括人食管鳞状细胞癌微环境中细胞的组成特征及其改变的细胞状态(Fig.6).用户可以通过“报告”模块导出完整的分析报告,以支持对结果的进一步解释和共享。此外,我们还可以在SeekSpace数据中显示基因表达和细胞类型的空间分布的可视化(Fig.6G-H).
更多实战复现可见:
零代码复现《Genome Medicine》|scRNA-seq解析CXCL16/CXCR6驱动驻留T细胞促进突触消除
《Nature Nanotechnol》都在用的零代码云平台
五、最后聊聊
由于不需要额外的安装或准备工作,也不依赖用户的编程技能或计算资源,在线分析平台已成为研究人员的首选。8-10用户只需通过浏览器访问,即可轻松上传自己的数据或选择平台提供的数据进行分析和可视化。11-13这种方法不仅大大减少了数据分析所花费的时间,还大大提高了研究效率,使研究人员能够更快地实现他们的研究目标。
本文重点介绍的SeekSoul Online是一个集成、模块化、用户友好的单细胞多组学数据分析云平台,旨在为研究人员提供全面的数据分析解决方案。该平台支持完整的分析管道,从细胞过滤、批量效应去除、聚类、细胞注释、差异基因表达 (DEG) 和富集分析,到特征分析、空间转录组数据的交互式可视化,以及广泛的高级分析,例如细胞间通讯、14-16基因共表达,17肿瘤细胞鉴定,18,19和伪时间分析。20,21该平台通过根据已发表文献创建的参考集大大提高了细胞注释的准确性。同时,其灵活的元数据管理功能满足了研究人员对细胞分类的个性化需求。
SeekSoul Online还提供了强大的交互式分析和报告功能,使用户能够独立进行深入的数据分析和挖掘。此外,其项目管理和协同分析能力极大地促进了项目管理效率和知识共享。因此,SeekSoul Online为单细胞多组学数据分析领域的研究人员提供了全面而强大的支持。

火山引擎开发者社区是火山引擎打造的AI技术生态平台,聚焦Agent与大模型开发,提供豆包系列模型(图像/视频/视觉)、智能分析与会话工具,并配套评测集、动手实验室及行业案例库。社区通过技术沙龙、挑战赛等活动促进开发者成长,新用户可领50万Tokens权益,助力构建智能应用。
更多推荐
 已为社区贡献3条内容
已为社区贡献3条内容





所有评论(0)